Слайд 2Меры активности
EC50 - полумаксимальная эффективная концентрация, означает концентрацию лиганда, которая вызывает эффект,

равный половине максимального возможного для данного лиганда
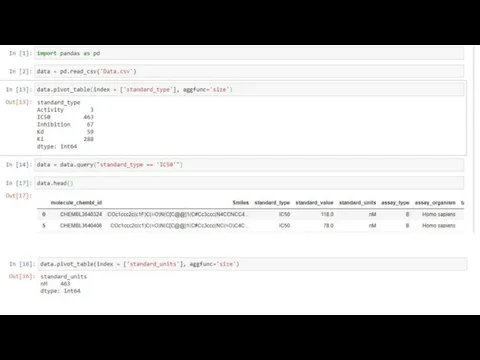
IC50 - является количественным индикатором, который показывает, сколько нужно лиганда—ингибитора для ингибирования биологического процесса на 50 %
Ki - концентрация конкурентного лиганда, при которой он связывается с половиной мест связывания, имеющихся на реакционном субстрате, при условии отсутствия агониста
Стандартные единицы измерения - nM
Слайд 4Выбираем свою меру активности
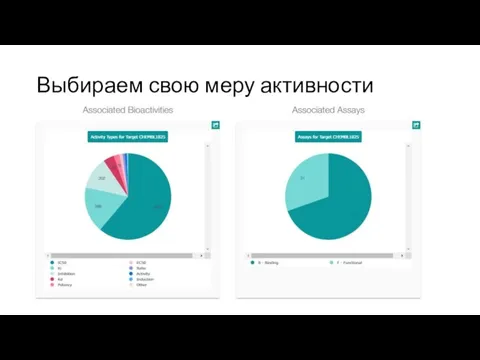
Слайд 6Is it active ? Probably…
IC50(compound 1) = 1000 nM
IC50(compound 2) = 100000

nM
Слайд 7Как узнать активно соединение или нет?
Посмотреть комментарий исследователя
Приблизительно определить активность используя «стандартные»

границы
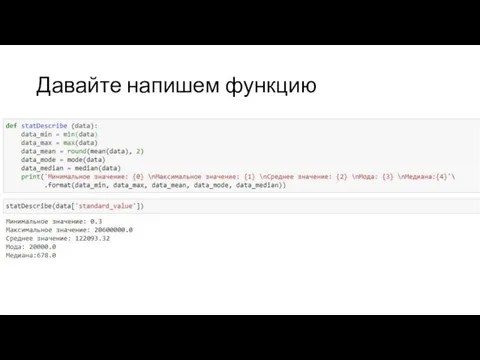
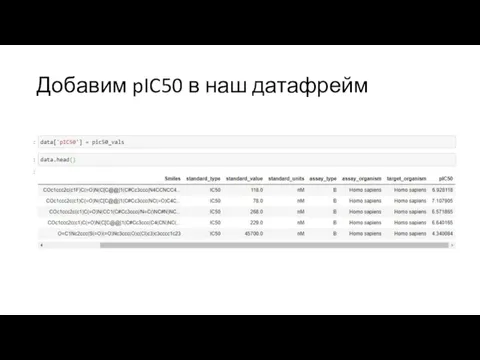
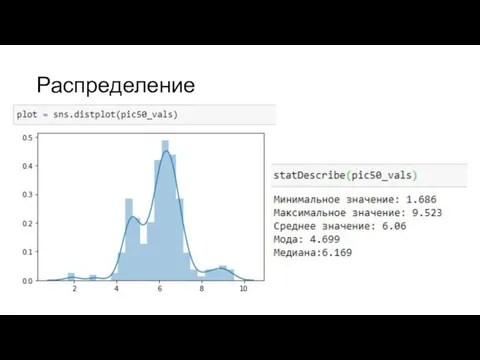
Слайд 10pIC50 (pKi, pEC50)
pIC50 = - log(IC50)
Как это работает?
Переводим в моли(М): IC50 =

100,000 nM *10^-9= 10^-4
Находим отрицательный логарифм:
–log(10^-4) = -(-4)log(10) = 4
3. Закономерность: чем выше pIC50, тем активнее средство.
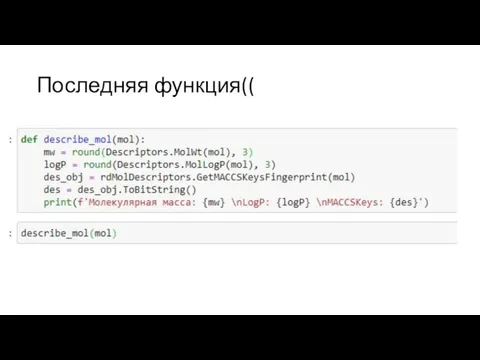
Слайд 11Давайте писать еще больше функций!!

Слайд 14«Стандартные» значения для IC50
IC50 < 1000 nM – активный компонент (6.0 и
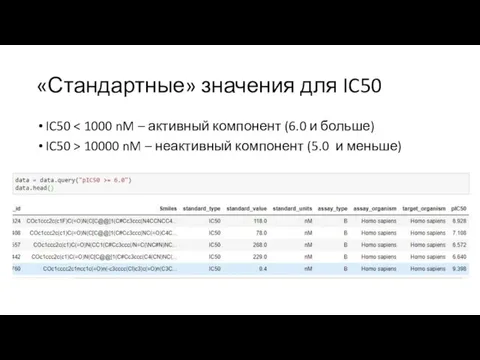
больше)
IC50 > 10000 nM – неактивный компонент (5.0 и меньше)
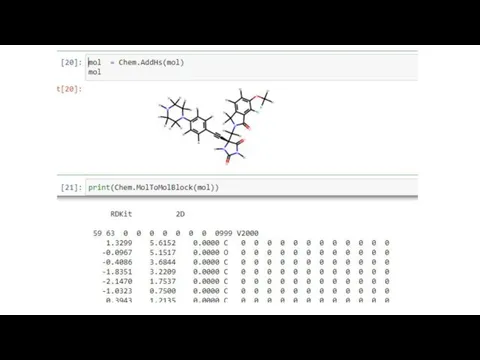
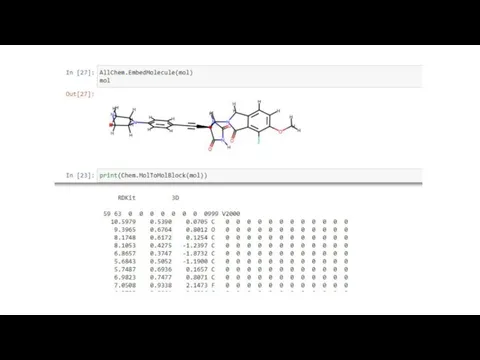
Слайд 15Введение в RDkit
Молекулярные дескрипторы

Слайд 19Идея:
1. Объединить схожие молекулы в кластеры.
2. Найти центральные молекулы каждого кластера.

3. Построить модель фармакофора
Слайд 20Молекулярные дескрипторы
Одномерные (1D): Растворимость, logP, молекулярная масса
Глобальный дескриптор: одно значение представляет все

соединение
Обычно недостаточны для применения в машинном обучении (ML)
Может быть добавлен к 2D-дескрипторам для улучшения молекулярного кодирования в ML.
Слайд 22Молекулярные дескрипторы
Двухмерные (2D): молекулярные графы, фрагменты молекул, окружения атомов.
Подробное представление отдельных частей

молекулы
Обнаружение так называемых отпечатков пальцев (фингерпринтов)
Очень часто используется в поиске сходства между молекулами и машинном обучении
Слайд 23Молекулярные дескрипторы
Основная идея – представить молекулу в виде бит-строки, где каждый бит
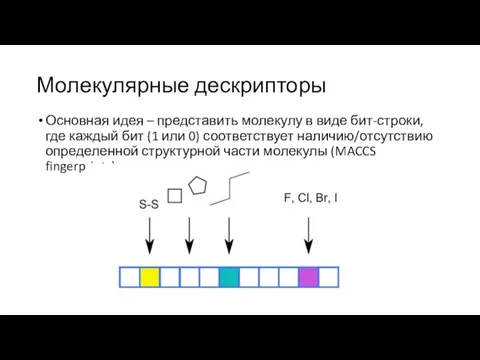
(1 или 0) соответствует наличию/отсутствию определенной структурной части молекулы (MACCS fingerprints)
Слайд 27Git
1. Регистрируемся на GitHub
2. Создаем репозиторий
3. Скачиваем Git на РС
4. Логинимся
5. Клонируем

репозиторий (git clone)
6. Копируем файлы проекта в репозиторий на РС
7. Проверяем статус (git status)
8. Добавляем файлы (подготовка коммита) (git add .)
9. Создаем коммит (git commit –m ‘initial commit’)
10. git push














 ВМ%20Собирова
ВМ%20Собирова Bezopasnaya_sreda_dlya_patsienta
Bezopasnaya_sreda_dlya_patsienta Неонатологические инкубаторы
Неонатологические инкубаторы Болезни органов дыхания и их предупреждение
Болезни органов дыхания и их предупреждение To i owo o bakteriach lek.-dent. Agnieszka grucka
To i owo o bakteriach lek.-dent. Agnieszka grucka Фундаментальные компоненты реабилитационной антинаркотической деятельности
Фундаментальные компоненты реабилитационной антинаркотической деятельности Уход за волосами. Перхоть
Уход за волосами. Перхоть Болезни, изменившие мир
Болезни, изменившие мир Ветряная оспа у детей
Ветряная оспа у детей Устройство МР-томографа
Устройство МР-томографа Молодёжь за безопасный секс
Молодёжь за безопасный секс Айткали Карина_легкие
Айткали Карина_легкие Отоларингология
Отоларингология Группы и категории инвалидности
Группы и категории инвалидности История возникновения ВБИ и борьба с ними
История возникновения ВБИ и борьба с ними Особенности гемодинамики у детей во внутриутробный период, период новорожденности и в первые годы жизни
Особенности гемодинамики у детей во внутриутробный период, период новорожденности и в первые годы жизни Как выбрать дату для кесаревого сечения
Как выбрать дату для кесаревого сечения Печень и поджелудочная железа
Печень и поджелудочная железа Микоплазмоз. Проблема микоплазмоза
Микоплазмоз. Проблема микоплазмоза Внутренние грыжи
Внутренние грыжи Острые нарушения мозгового кровообращения (ОНМК)
Острые нарушения мозгового кровообращения (ОНМК) Фізичний розвиток. Задача
Фізичний розвиток. Задача Острый гематогенный остеомиелит
Острый гематогенный остеомиелит Функциональная анатомия спинномозговых нервов
Функциональная анатомия спинномозговых нервов Начало лечения гемолитической болезни
Начало лечения гемолитической болезни Безинъекционная реструктуризация кожи
Безинъекционная реструктуризация кожи Белсенді туризмде тамақтану
Белсенді туризмде тамақтану Неврологическая симптоматика болезни Уиппла
Неврологическая симптоматика болезни Уиппла